🧬 Práctica de Laboratorio 2 — Ficheros
Esta práctica aborda el manejo, lectura y procesamiento de ficheros en bioinformática utilizando Python y Biopython. A lo largo del trabajo se desarrollan ejercicios orientados al tratamiento de secuencias biológicas reales en formato FASTA, así como la descarga y visualización de estructuras proteicas en formato PDB. Además, se incorporan representaciones interactivas con py3Dmol para explorar modelos tridimensionales de proteínas.
Descarga del ZIP del proyecto
Haz clic para obtener el paquete completo del proyecto:
Repositorio oficial
Puedes consultar el repositorio completo aquí:
- Práctica de Laboratorio 2: https://github.com/giselabcruz/P2_Ficheros
Ejercicio 1 — Manejo de secuencias FASTA
En este ejercicio se realizó el procesamiento de secuencias de ADN en formato FASTA mediante Python. Entre las tareas desarrolladas se encuentran:
✔ Lectura de secuencias de ADN desde un archivo FASTA
✔ Cálculo del contenido GC
✔ Traducción automática ADN → proteína
✔ Escritura de las proteínas generadas en un nuevo archivo FASTA
✔ Visualizaciones complementarias (histogramas, comparativas, etc.)
Archivos utilizados:
- Entrada:
input/dna_seqs.fasta - Salida:
output/proteins.fasta
Ejercicio 2 — Búsqueda y visualización de proteínas
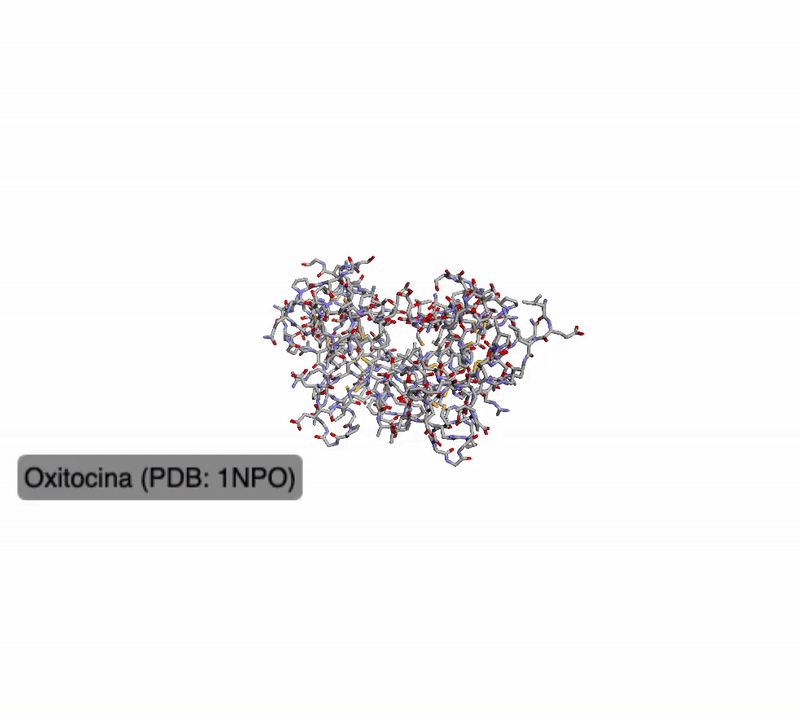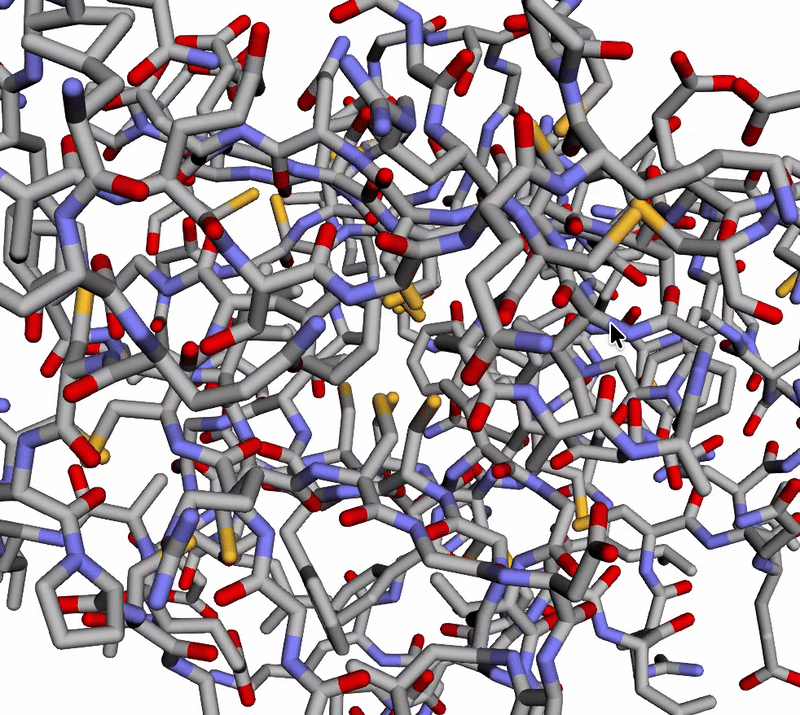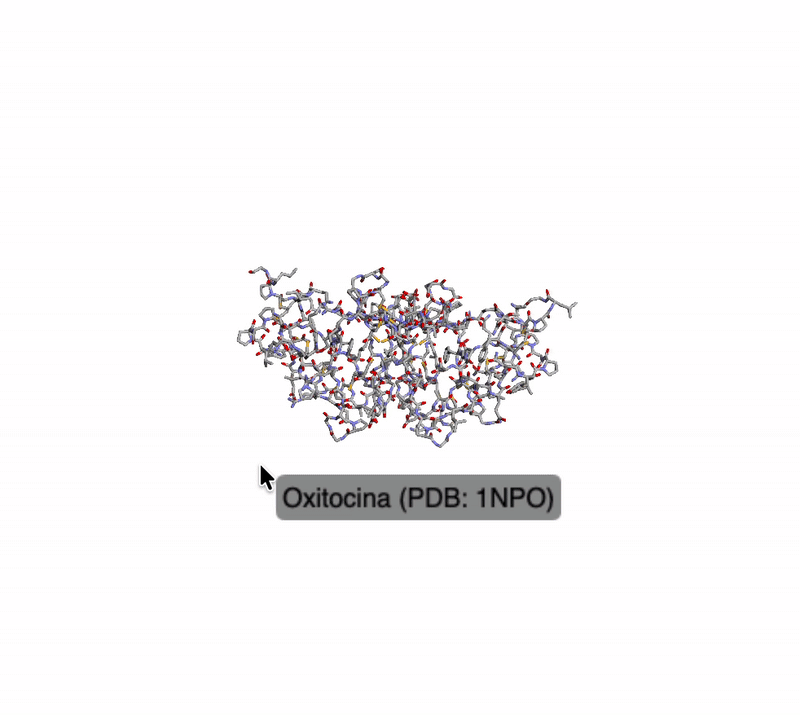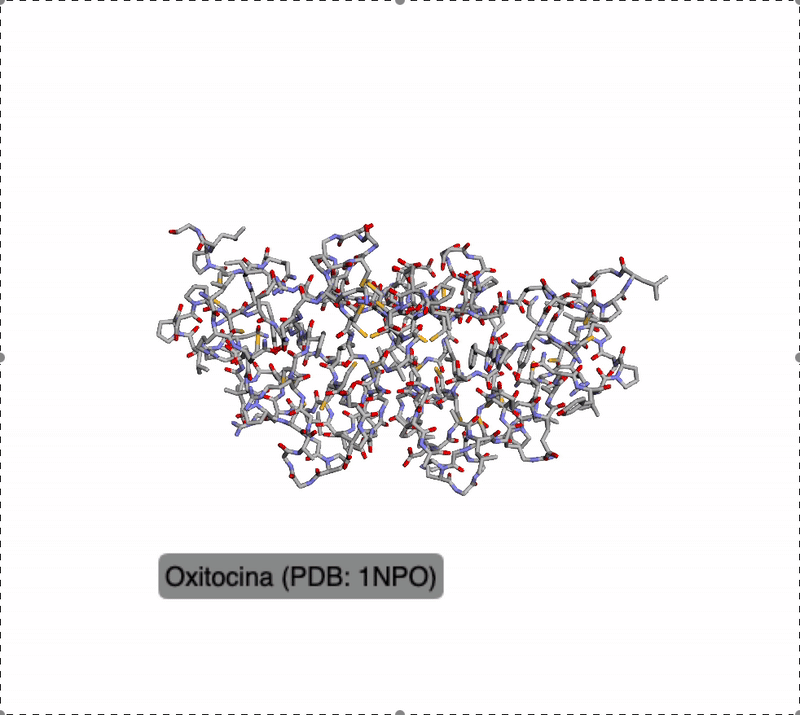
En este apartado se trabajó con ficheros PDB y visualización 3D con py3Dmol de proteínas obtenidas del Protein Data Bank.
Proteínas analizadas:
- Oxitocina — PDB: 1NPO
- Colágeno — PDB: 1CAG
- Queratina — PDB: 4ZRY

Colágeno

Queratina